La transcription
La transcription est le mécanisme par lequel les ARN sont synthétisés. Ces derniers sont répartis en 3 classes qui sont produites par transcription de l'ADN aussi bien chez les procaryotes que chez les eucaryotes:
L'ARNm: copie transitoire d'une portion de l'ADN correspondant à un ou plusieurs gènes et porte l'information génétique qui est destiné à être traduite en protéines au niveau des ribosomes.
L'ARNr: son assemblage avec les protéines forme les ribosomes, machines cellulaire responsable de la synthétise protéique.
L'ARNt: intervient aussi dans la synthèse des protéines où ils apportent les acides aminés vers les ribosomes.
La transcription de l'ADN en ARNm est suivie de sa traduction en protéines. Par contre, ce n'est pas le cas pour l'ARNr et l'ARNt qui sont uniquement transcrits mais pas traduits.
Dans cette étape un ARNm est formé par copie d'une portion d'ADN. Étant donné que:
Tout l'ADN n'est pas transcrit, mais uniquement certaines portions d'ADN.
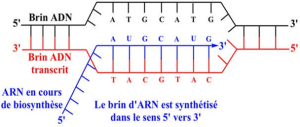
Seul l'un des 2 brins d'ADN est copié, mais ce n'est pas toujours le même brin. En effet, pour certains gènes se sera un brin, pour d'autres gènes se sera l'autre brin (fig.33). L'ARN est produit en utilisant le brin matrice et la molécule d'ARN synthétisée est une copie du brin non matrice (appelée aussi brin sens positif ou brin codant).
La synthèse d'un ARNm est toujours effectuée dans le sens conventionnel 5' – 3' et de façon antiparallèle et complémentaire par rapport au brin d'ADN transcrit.
Les éléments nécessaires pour la transcription
Des nucléotides triphosphates : ATP, GTP, CTP et UTP.
L'ARN polymérase est l'enzyme qui permet de souder les nucléotides les uns aux autres pour former ce polymère qui est l'ARN messager.
L'ADN matrice qui est indispensable pour la synthèse de l'ARNm.
Transcription chez les procaryotes
Fondamental :
Chez ces organismes la transcription est divisée en 3 phases : initiation, élongation et terminaison. L'ARN polymérase est l'enzyme qui est responsable de la transcription.[1]
Initiation
La transcription est un phénomène sélectif : tout l'ADN n'est pas transcrit. Le problème consiste à savoir comment les séquences à transcrire seront reconnues par l'ARN polymérase. En fait, les questions qui se posent donc:
Qu'est ce qui indiquera qu'une région d'ADN doit commencer à être transcrite de même ? Qu'est ce qui indiquera que la transcription doit se terminer ?
- Promoteur : La transcription ne peut démarrer de façon aléatoire, mais elle doit être initiée au début d'un gène. Le signal de début de transcription est le « promoteur ». C'est une région d'ADN comprenant environ 40 paires de nucléotides situés juste avant le début de la région ou démarrera la transcription. Chez E. coli, les séquences de nucléotides ont été déterminées pour plus de 100 promoteurs de différents gènes. Une comparaison de séquences d'ADN de nombreux promoteurs puissants révèle que la polymérase reconnaît deux séquences d'ADN très conservées, longues de 6 nucléotides chacune qui sont situées en amont du site d'initiation et séparées l'une de l'autre par environ 17 nucléotides d'ADN non reconnu. On dit aussi que ces séquences de composition très voisine présentent une homologie. Elles sont appelées séquences consensus (similitude de séquences) (fig. 35)
- Séquence « -35 » : est située approximativement à 35 paires de nucléotides en amont du point de départ de la transcription, représentée par 3 bases hautement conservées (supérieure à 75%). TTGACA (avec T82% T84% G78% A65% C54% A45%).
- Séquence « -10 » : est située à environ 10 paires de nucléotides en amont du point de départ de la transcription (de –12 à –7 dans l'exemple) représentée par 3 bases qui sont également hautement conservées. TATATT (T80% A95% T45% A60% T50% T96%). L'association de l'ARN polymérase au promoteur :
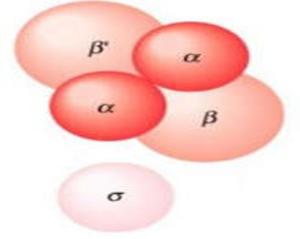
La sous unité sigma de l'ARN polymérase permet une reconnaissance spécifique du promoteur (l'absence de la sous unité sigma, augmente l'affinité de la polymérase pour les régions non promotrices).
L'enzyme se fixe au promoteur, elle commence par former un complexe d'initiation au sein duquel l'ADN demeure sous forme double hélice, l'enzyme recouvre une soixantaine de paires de bases et du promoteur, y compris les boites –35 et –10 (fig. 36).
Pour permettre à la transcription de commencer, la double hélice se dissocie partiellement au niveau de la boite –10, riche en liaison faibles A-T, et on aura à ce moment un complexe promoteur ouvert.
La sous unité sigma se dissocie ensuite du complexe promoteur et la sous-unité béta prend le relais pour synthétiser la première liaison phosphodiester.
Élongation
Au cours de l'élongation, l'ARN polymérase se déplace le tout au long de la molécule d'ADN en détruisant des liaisons hydrogène H et en déroulant la double hélice au cours de sa progression (on peut représenter cette enzyme comme un curseur se déplaçant sur une fermeture éclair). L'enzyme ajoute des ribonucléotides à l'extrémité 3' de la molécule d'ADN avec un ordre d'addition déterminé par l'ordre des bases sur le brin matrice.
L'ARN polymérase commence sa progression sur le brin matrice dans le sens 5' vers 3'. Dans la plupart des cas une séquence dite 5'UTR (untranslated region) de taille variable est transcrite avant la séquence codante. De façon similaire, après la séquence codante, une séquence non codante appelée séquence de queue (trailer) ou 3' UTR est transcrite avant la fin de la transcription (fig. 37).
Terminaison
La transcription chez les procaryotes lorsque l'ARN polymérase arrive à des points spécifiques situés après la fin de la séquence codante.
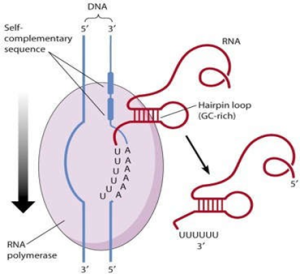
Chez E. coli, la terminaison a lieu au niveau de séquences appelées palindromes. Cette région est immédiatement suivie d'une courte séquence riche en bases A et T (le brin d'ADN qui sera transcrit contient à ce niveau plusieurs A).
La transcription de la région à symétrie palindrome donnera donc une séquence d'ARNm capable de self-complémentarité, l'ARNm se terminera par une boucle. C'est cette boucle en épingle à cheveux qui serait responsable de l'arrêt de la transcription.
Un autre mécanisme de terminaison, fait appel une protéine appelée Rho (ρ) est impliquée dans la destruction de l'appariement entre les bases de l'ARN et de l'ADN matrice lorsque l'ARN polymérase s'arrête après le motif en épingle à cheveux.
La terminaison enfin de la transcription correspond à la libération du transcrit.